4月7日,浙江万里学院生物与环境学院夏亦荠与张海磊研究团队于Nature Communications发表题为《High-resolution mapping reveals features of bacterial NAD-capped RNAs and stress-responsive transcription initiation》的研究论文,该研究构建了高精度的细菌NAD加帽RNA(NAD-RNA)鉴定体系,绘制了大肠杆菌NAD-RNA的全转录组高分辨率图谱。

NAD⁺作为广泛存在的代谢辅酶,近年来被发现可形成RNA 5′端加帽结构(NAD-cap),暗示其在基因表达调控中起到重要作用;然而,既有鉴定技术在5′端定位精度与短链RNA检出率方面的两个局限,严重制约该领域的深入发展。为此,本研究开发了两套互补技术:1)pNAD‑seq:通过ADPRC/SPAAC反应将生物素高效且特异性标记NAD+帽结构(设对照消除背景),经链霉亲和素富集及NudC介导的去帽暴露5′‑pA,通过接头序列连接的方式构建测序文库,从而实现NAD‑RNA的5′端腺苷(A)的精确鉴定,同时显著提升短链NAD-RNA检出能力;2)NAD‑linkSeq:基于同样的富集策略,经去帽与接头连接后,将完整NAD-RNA转化成全长cDNA,利用Nanopore 测序平台对其进行测序,实现NAD‑RNA全长序列的精准测定(图1)。
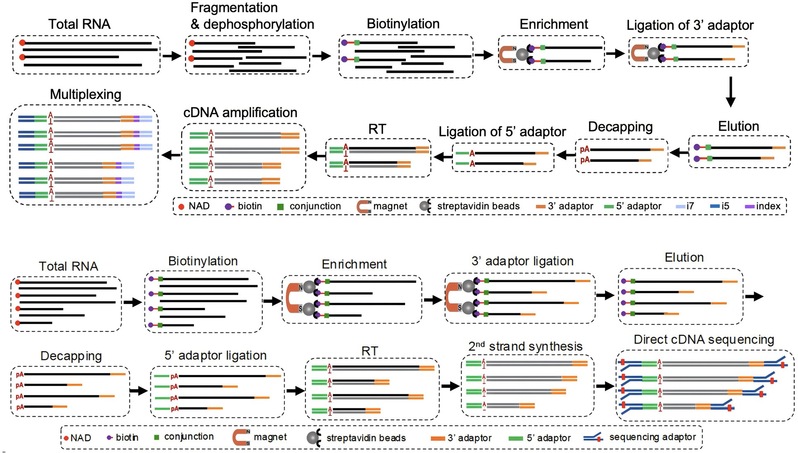
图1. pNAD-seq(上)和NAD-linkSeq(下)流程图
高分辨率图谱不仅鉴定出大肠杆菌中新的NAD‑RNA种类(包括tRNA、rRNA及反义RNA),更在TSS邻近区域(−2至+2)发现保守序列RDAY,统计发现带此序列的启动子通常产生较高NAD⁺加帽比例的转录本,为理解NAD加帽的分子机制提供了新的线索(图2)。值得注意的是,在氮源限制胁迫下,NAD‑RNA表现出显著的TSS切换与替代启动子使用现象,揭示其在感知代谢应激并重塑转录起始中具有潜在作用。
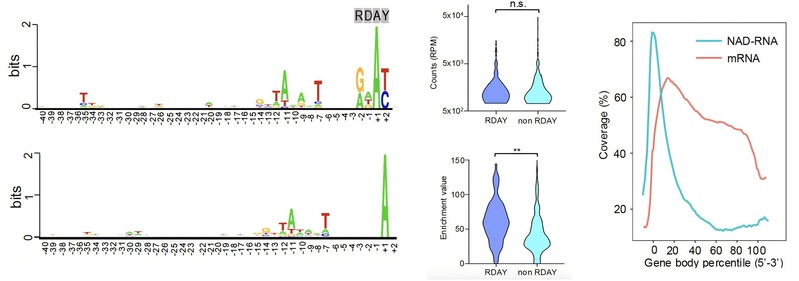
图2. 保守序列与转录本长度特征
本研究建立了可拓展至真核生物的高精度NAD‑RNA鉴定方案,并呈现了目前最完备的大肠杆菌NAD‑RNA图谱,为揭示NAD⁺加帽在转录调控中的生物学功能提供了强有力的数据与方法支持。
本研究以浙江万里学院为第一完成单位。论文第一作者为张海磊博士,通讯作者由夏亦荠教授、宁波东方理工大学蔡宗苇教授和张海磊博士共同担任。该研究得到了浙江万里学院科研启动经费、香港研究资助局合作研究基金及优配研究基金等项目的资助。
